Künstliche Intelligenz
Schwarmlernen entschlüsselt Biomoleküle
- von Jennifer Meina
- 26.07.2021
Sie werden häufig als „Bausteine des Lebens“ bezeichnet: Biomoleküle. Um ihre Funktion im Körper zu verstehen und zu nutzen, muss man ihre Struktur kennen. Eine aufwändige und teils ungenaue Angelegenheit. Hier setzt die neue Methode an, die an der UDE mit anderen deutschen Forschungszentren erarbeitet wurde – mit Hilfe von Künstlicher Intelligenz. Ihre Ergebnisse haben die Forschenden nun in Nature Machine Intelligence* veröffentlicht.
Mit der Nahrung aufgenommen, gelangen Biomoleküle in den Körper und werden in chemische Verbindungen – also Biomoleküle wie Fette, Proteine oder Kohlenhydrate – zerlegt. Interessant wird die Frage, wie sie aufgebaut sind, vor allem dann, wenn es etwa um die molekulare Ursache von Krankheiten geht. Das Problem: Um die Struktur der nanogroßen Biomoleküle aufzulösen, braucht es aufwendige Experimente. Doch selbst dann sind die Auswertungen nicht immer eindeutig – die gemessenen Daten benötigen eine umfangreiche Interpretation. UDE-Professor Alexander Schug, Leiter der Arbeitsgruppe Computergestützte Strukturbiologie, verdeutlicht das mit einem Beispiel: „Ein Schattenwurf kann durch unterschiedliche Formen hervorgerufen werden. Hier haben wir die Messdaten, wie das Biomolekül auf die Untersuchung reagiert, aber wissen nicht direkt, wie das Biomolekül aussieht.“
Hier kommt die Künstliche Intelligenz ins Spiel, die das Team der UDE gemeinsam mit dem Forschungszentrum Jülich, dem Karlsruher Institut für Technologie und dem Deutschen Krebsforschungszentrum erarbeitet hat. Die Messdaten werden durch ein physik-basiertes Modell des Biomoleküls im Computer ergänzt. „Um in der Analogie des Schattenwurfs zu bleiben, fragen wir uns: Welche Biomolekülform könnte einen solchen Schatten erzeugen und ist gleichzeitig physikalisch stabil?“
Die Methode beruht auf Schwarmlernen: Ein Computer simuliert viele Mitglieder eines großen Schwarms gleichzeitig, wobei jedes Mitglied eine andere Gewichtung von Messwerten und physikalischem Modell testet. Dabei stehen alle Schwarmmitglieder untereinander in Kontakt und im permanenten Austausch von Parameterkombinationen. „Sie lernen, welche Kombinationen gut funktionieren und können immer besser eingrenzen, welche weiteren vielversprechenden Kombinationen es gibt. Dies führt dann zur gesuchten Struktur.“ Dadurch nutzt die neue Methode die Rechenzeit sehr effizient und liefert gleichzeitig hoch akkurate Strukturen.
Künftig könnte diese Methode helfen, Krankheiten zu therapieren, die auf molekularer Ebene wirken, wie Alzheimer oder Huntington. Auch der Einsatz in Materialsimulationen ist denkbar.
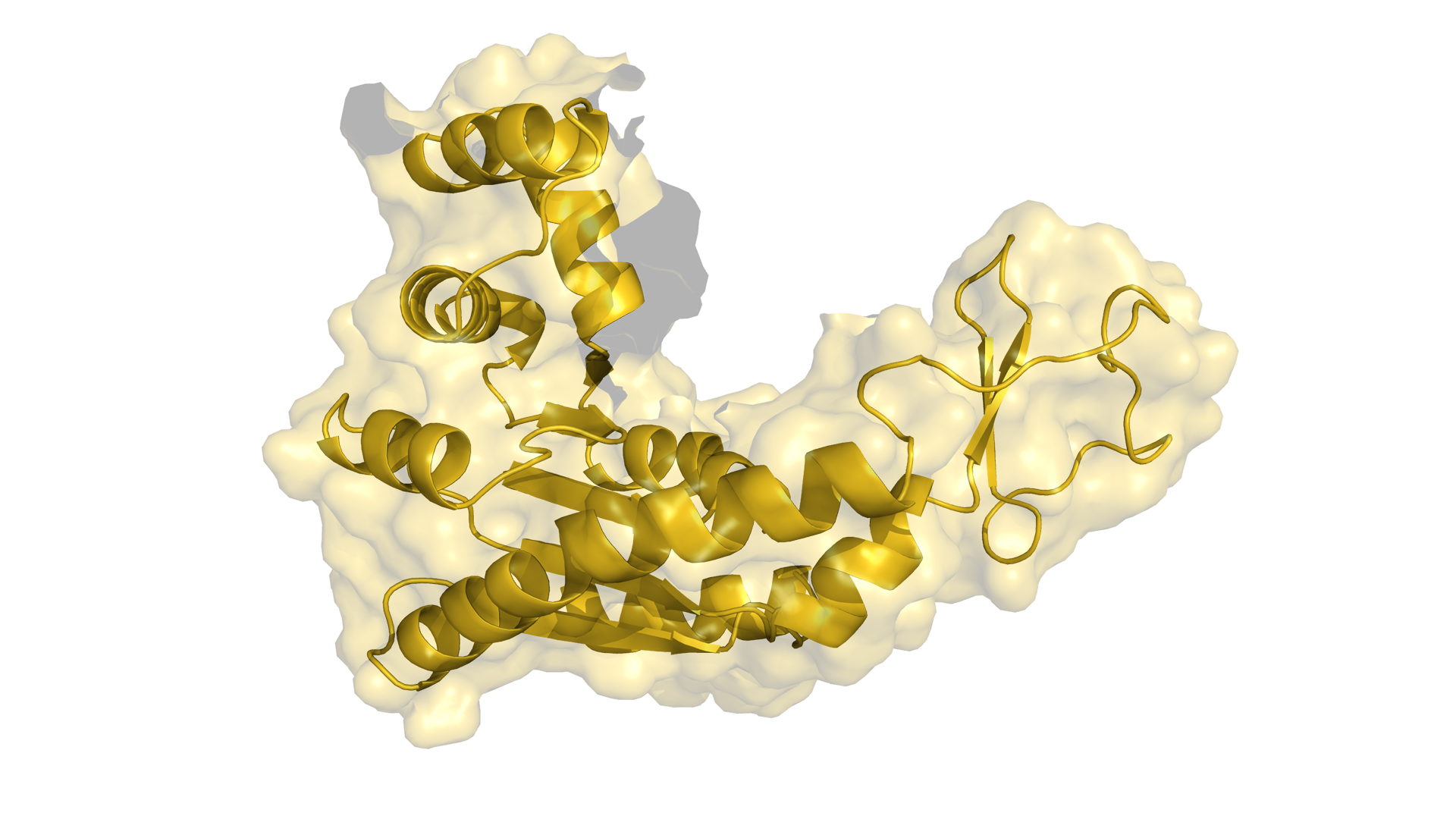
Im Bild:
Biomoleküle sind für zahlreiche Funktionen im Körper zuständig. Ihre Struktur zu entschlüsseln, ist nicht immer einfach.
* Weiel, M., Götz, M., Klein, A., Coquelin, D., Floca, R., Schug, A. (2021) FLAPS: Dynamic particle swarm optimization of biomolecular simulation parameters with flexible objective functions. Nature Machine Inteligence, DOI: 10.1038/s42256-021-00366-3.
www.nature.com/articles/s42256-021-00366-3
Weitere Informationen:
Prof. Dr. Alexander Schug, Computational Structural Biology, Tel. 02461/61-9095, alexander.schug@uni-due.de
Redaktion: Jenifer Meina, Tel.0203/37 9-1205, jennifer.meina@uni-due.de
